Tabela Comparativa Ampliada: Criacionismo vs. Evolucionismo
|
Nº
|
Fenômeno Citado
|
Previsão/Expectativa Criacionista
|
Previsão/Expectativa Evolucionista
|
Situação Observada (segundo o artigo)
|
Resultado Comparativo
|
|
1
|
Tecidos moles em fósseis
|
Possíveis se os fósseis forem relativamente recentes.
|
Não deveriam existir após dezenas de milhões de anos.
|
Presença de tecidos e biomoléculas reportadas em fósseis.
|
Favorece previsão criacionista
|
|
2
|
Explosão de mutações entre 5–10 mil anos
|
Pico mutacional recente após evento energético/catastrófico/radioativo.
|
Taxas mutacionais constantes distribuídas ao longo de milhões de anos como base dos relogios moleculares e radiométricos
|
Evidências interpretadas como pico mutacional recente.
|
Favorece previsão criacionista que antecipou pelo grupo RATE aceleração de decaimento no dilúvio.
|
|
3
|
Estratos sedimentares
|
Deposição rápida formando camadas extensas, largas e espessas em tiras plano paralelas sem erosão intercamadas, resultantes de transgressões e regressões marinhas globais.
|
Formação lenta e gradual ao longo de longos períodos.
|
Grandes pacotes estratificados contínuos que apontam para catástrofes.
|
Favorece previsão criacionista
|
|
4
|
Camada Ediacarana
|
Primeiros depósitos sedimentares pós-evento com assinatura energética e radioativa.
|
Evolução gradual de biota pré-Cambriana.
|
Primeira camada associadas a evidências geoquímicas e picos de radioatividade.
|
Favorece previsão criacionista
|
|
5
|
Vida curta do DNA
|
O DNA não deveria sobreviver por milhões de anos.
|
O DNA não poderia ser encontrado em fósseis antigos.
|
Favorece previsão criacionista
|
|
|
6
|
C-14 em rochas antigas
|
Presença de carbono-14 indicaria idade recente.
|
Não deveria existir C-14 detectável em rochas de milhões de anos.
|
Favorece previsão criacionista
|
|
|
7
|
Gigantismo fóssil
|
Média de organismos antigos maiores que os descendentes atuais (degeneração).
|
Tendência evolutiva progressiva ou variável, sem um padrão definido de gigantismo no passado.
|
Favorece previsão criacionista
|
|
|
8
|
Redução do cérebro humano
|
Degeneração recente após uma população inicial mais capaz.
|
Aumento progressivo da capacidade craniana e inteligência ao longo da evolução.
|
Variações com redução média do volume cerebral em períodos recentes.
|
Favorece previsão criacionista
|
|
9
|
Genealogias antigas
|
Cronologia humana curta, na casa de milhares de anos.
|
Origem humana muito mais antiga, na casa de centenas de milhares de anos.
|
Genealogias antigas (bíblicas e de outras culturas) descrevem linhagens curtas.
|
Favorece previsão criacionista
|
|
10
|
Paleotocas gigantes
|
Atividade de megafauna em um passado recente (milhares de anos).
|
Atividade de megafauna em um passado muito mais distante (dezenas de milhares a milhões de anos).
|
Datação de paleotocas no Brasil em torno de 10.000 anos.
|
Favorece previsão criacionista
|
|
11
|
Estase morfológica
|
“Tipos básicos” criados permanecem relativamente estáveis.
|
Mudança gradual e contínua com muitas formas transicionais.
|
Padrão dominante no registro fóssil é de aparecimento súbito e estase.
|
Favorece previsão criacionista
|
|
12
|
Explosão Cambriana
|
Aparecimento abrupto de formas de vida complexas.
|
Longo período de evolução de precursores mais simples.
|
Maioria dos filos animais modernos aparece sem precursores claros.
|
Favorece previsão criacionista
|
|
13
|
Entropia genética
|
Genomas acumulam mutações deletérias, levando à degeneração.
|
Seleção natural gera novas informações e complexidade.
|
Aumento de doenças genéticas e declínio geral do fitness.
|
Favorece previsão criacionista
|
|
14
|
Funcionalidade do DNA não codificante
|
Grandes porções do genoma terão funções importantes (design integrado).
|
Grandes porções do genoma são “DNA lixo” não funcional.
|
Projeto ENCODE e outros estudos revelam ampla funcionalidade bioquímica.
|
Favorece previsão criacionista
|
|
15
|
Complexidade irredutível
|
Sistemas complexos como o flagelo bacteriano foram criados completos.
|
Sistemas complexos evoluem de precursores mais simples.
|
Ausência de precursores funcionais para sistemas como o flagelo.
|
Favorece previsão criacionista
|
|
16
|
“Eva Mitocondrial” recente
|
Relógio molecular do DNAm aponta para uma origem recente da humanidade.
|
Relógio molecular do DNAm aponta para uma origem há centenas de milhares de anos.
|
Taxas de mutação observadas em tempo real (pedigree) apontam para uma “Eva” em torno de 6.000-10.000 anos.
|
Favorece previsão criacionista
|
|
17
|
Origem recente de variantes deletérias
|
Maioria das mutações deletérias surgiu nos últimos 5.000-10.000 anos.
|
Mutações deletérias surgiram e foram selecionadas ao longo de milhões de anos.
|
Análise de exomas humanos modernos confirma a origem recente da maioria das variantes.
|
Favorece previsão criacionista
|
|
18
|
Início do Universo (Big Bang)
|
O universo teve um início, conforme previsto em relatos criacionistas.
|
Universo era considerado eterno e estático (modelo do estado estacionário).
|
Teoria do Big Bang confirma que o universo teve um começo.
|
Favorece previsão criacionista
|
|
19
|
Ajuste fino do universo
|
Constantes fundamentais da natureza são finamente ajustadas para a vida, apontando para um Designer.
|
O ajuste fino é um acaso ou explicado por hipóteses como o multiverso.
|
A precisão das constantes físicas para permitir a vida é um fato científico estabelecido.
|
Favorece previsão criacionista
|
|
20
|
Degeneração do gene TP53
|
Mutações deletérias no TP53 são recentes e ausentes em espécies mais antigas/robustas.
|
Mutações no TP53 ocorreriam aleatoriamente ao longo da história evolutiva.
|
Variações deletérias do TP53 são encontradas no homem moderno, mas não em Neandertais ou mamutes.
|
Favorece previsão criacionista
|
|
21
|
Polistratismo fossilífero
|
Fósseis que atravessam múltiplas camadas sedimentares indicam soterramento rápido.
|
Soterramento lento e gradual não permitiria a preservação de um organismo em múltiplas camadas.
|
Troncos de árvores fossilizados em pé atravessando várias camadas de carvão e rocha.
|
Favorece previsão criacionista
|
|
22
|
Dobramentos de camadas sem fratura
|
Camadas sedimentares foram dobradas enquanto ainda estavam moles e úmidas.
|
As camadas foram dobradas muito tempo depois de se solidificarem (litificadas).
|
Grandes formações rochosas dobradas (ex: Grand Canyon) sem evidência de fratura.
|
Favorece previsão criacionista
|
|
23
|
Ausência de erosão entre camadas
|
Camadas foram depositadas rapidamente, uma sobre a outra, sem tempo para erosão.
|
Deveria haver evidência de longos períodos de erosão entre as camadas.
|
Contatos planos e nítidos (“paraconformidades”) entre camadas supostamente separadas por milhões de anos.
|
Favorece previsão criacionista
|
|
24
|
Limite de idade do campo magnético da Terra
|
O campo magnético está decaindo rapidamente, limitando a idade da Terra a milhares de anos.
|
O campo magnético se auto-sustenta e inverte sua polaridade ao longo de milhões de anos.
|
Medições contínuas desde 1835 mostram um decaimento consistente do campo magnético.
|
Favorece previsão criacionista
|
|
25
|
Hélio em zircões
|
Retenção de hélio em cristais de zircão indica uma idade jovem para as rochas graníticas.
|
O hélio, um gás leve, deveria ter escapado completamente ao longo de milhões de anos.
|
Quantidades significativas de hélio encontradas em zircões de perfurações profundas.
|
Favorece previsão criacionista
|
|
26
|
Cometas de curto período
|
A existência de cometas de curto período sugere um sistema solar jovem.
|
Deveria haver uma fonte (como a Nuvem de Oort) para reabastecer os cometas.
|
A Nuvem de Oort permanece uma hipótese não observada diretamente.
|
Favorece previsão criacionista
|
|
27
|
Acúmulo de sedimento no fundo do mar
|
A quantidade de sedimento nos oceanos é consistente com uma deposição de poucos milhares de anos.
|
A taxa de deposição ao longo de bilhões de anos deveria ter resultado em uma camada muito mais espessa.
|
A espessura média do sedimento oceânico é muito menor do que o esperado pelo modelo antigo.
|
Favorece previsão criacionista
|
|
28
|
Salinidade dos oceanos
|
A concentração de sal nos oceanos é consistente com uma idade de poucos milhares de anos.
|
Os oceanos deveriam ser muito mais salgados se tivessem bilhões de anos.
|
A taxa de entrada de sal nos oceanos é muito maior que a taxa de saída.
|
Favorece previsão criacionista
|
|
29
|
“Fósseis vivos”
|
Organismos permanecem essencialmente inalterados por supostos milhões de anos.
|
Organismos deveriam mostrar mudança evolutiva significativa ao longo do tempo.
|
Exemplos como o celacanto, o tuatara e a árvore Ginkgo são morfologicamente idênticos aos seus fósseis.
|
Favorece previsão criacionista
|
|
30
|
Origem da agricultura
|
A agricultura surgiu subitamente em várias partes do mundo há cerca de 10.000 anos.
|
A agricultura deveria ter se desenvolvido gradualmente ao longo de um período muito mais longo.
|
Registros arqueológicos mostram um aparecimento súbito e recente da agricultura.
|
Favorece previsão criacionista
|
|
31
|
Crescimento populacional humano
|
A população humana atual pode ser alcançada a partir de um pequeno grupo inicial em poucos milhares de anos.
|
A humanidade existe há centenas de milhares de anos, o que implicaria uma população muito maior ou taxas de crescimento irrealisticamente baixas.
|
Cálculos de crescimento populacional são consistentes com uma cronologia curta.
|
Favorece previsão criacionista
|
|
32
|
Linguagens humanas
|
As linguagens se diversificam e degeneram a partir de uma fonte comum (similar a Babel).
|
As linguagens evoluem de sons primitivos para sistemas complexos.
|
Estudos linguísticos mostram que as línguas antigas eram frequentemente mais complexas que as modernas.
|
Favorece previsão criacionista
|
|
33
|
Simbiose
|
Relações simbióticas complexas (ex: figo e vespa) tiveram que surgir completas e funcionais.
|
Relações simbióticas co-evoluíram gradualmente.
|
A interdependência obrigatória em muitos sistemas simbióticos desafia uma explicação passo a passo.
|
Favorece previsão criacionista
|
|
34
|
Metamorfose
|
Processos de múltiplos estágios como a metamorfose (lagarta para borboleta) foram projetados.
|
A metamorfose evoluiu gradualmente, com cada estágio sendo viável.
|
A transição radical na metamorfose completa é difícil de explicar por pequenas modificações sucessivas.
|
Favorece previsão criacionista
|
|
35
|
Instintos complexos
|
Comportamentos instintivos complexos (ex: migração de aves, construção de teias de aranha) são programados.
|
Instintos evoluem gradualmente a partir de comportamentos mais simples.
|
A complexidade e precisão de muitos instintos inatos desafiam uma origem gradual.
|
Favorece previsão criacionista
|
|
36
|
Bio-luminescência
|
Reações químicas complexas para produção de luz foram projetadas.
|
A bio-luminescência evoluiu de forma independente várias vezes por caminhos graduais.
|
A complexidade dos sistemas de luciferina-luciferase aponta para um design.
|
Favorece previsão criacionista
|
|
37
|
O código genético
|
O código genético é uma linguagem universal e otimizada, produto de inteligência.
|
O código genético evoluiu de uma forma mais simples e primitiva.
|
A universalidade e a otimização do código genético para minimizar erros são características de design.
|
Favorece previsão criacionista
|
|
38
|
Origem da sexualidade
|
A reprodução sexuada, com seus mecanismos complexos e complementares, foi projetada.
|
A reprodução sexuada evoluiu a partir da reprodução assexuada.
|
A origem da reprodução sexuada, com a necessidade de dois sexos compatíveis surgindo simultaneamente, é um grande enigma para a evolução.
|
Favorece previsão criacionista
|
|
39
|
Lacunas no registro fóssil
|
As lacunas entre os principais grupos de organismos são reais e representam a ausência de ancestrais comuns.
|
As lacunas são artefatos de um registro fóssil incompleto e serão preenchidas com mais descobertas.
|
Apesar de 150 anos de busca, as lacunas sistemáticas entre os grandes filos e classes persistem.
|
Favorece previsão criacionista
|
|
40
|
Consciência humana
|
A consciência, a moralidade e a racionalidade são dons de um Criador.
|
A consciência é um epifenômeno do cérebro que emergiu por processos evolutivos.
|
A natureza imaterial da consciência (o “difícil problema da consciência”) não é explicada por processos puramente materialistas.
|
Favorece previsão criacionista
|
|
41
|
Beleza na natureza
|
A beleza estética na natureza (ex: flores, penas de pavão) existe para ser apreciada, um sinal de um Criador artístico.
|
A beleza é um subproduto da seleção sexual ou de outras funções utilitárias.
|
A existência de beleza que excede qualquer propósito puramente utilitário (beleza “gratuita”) aponta para o design.
|
Favorece previsão criacionista
|
Análise Quantitativa (Baseada nos 41 Pontos)
|
Categoria
|
Quantidade
|
|
Previsões alinhadas ao modelo criacionista
|
41
|
|
Previsões alinhadas ao modelo evolucionista
|
0
|
Cálculo do Valor Preditivo (Dentro Deste Conjunto de Dados)
Modelo Criacionista:
VP = 41 / 41 = 1.0 (100%)
Modelo Evolucionista:
VP = 0 / 41 = 0.0 (0%)
Conclusão da Análise
Tabela comparativa entre modelo criacionista vs evolucionista quanto a capacidade de previsão
| Nº | Fenômeno citado | Previsão/expectativa criacionista | Previsão/expectativa evolucionista | Situação observada (segundo os dados citados) | Resultado comparativo |
|---|---|---|---|---|---|
| 1 | Tecidos moles em fósseis | Possíveis se os fósseis forem relativamente recentes | Não deveriam existir após dezenas de milhões de anos | Presença de tecidos e biomoléculas reportadas em fósseis | Favorece previsão criacionista |
| 2 | Explosão de mutações entre 5–10 mil anos | Pico mutacional recente após evento energético/catastrófico | Taxas mutacionais constantes distribuídas ao longo de milhões de anos | Evidências interpretadas como pico mutacional recente | Favorece previsão criacionista |
| 3 | Estratos sedimentares | Deposição rápida formando camadas extensas, largas e espessas em tiras estratos resultantes de transgressões e regressões continentais e globais do mar agitado | Formação lenta ao longo de longos períodos | Grandes pacotes estratificados contínuos só se formam por catástrofes globais | Favorece previsão criacionista |
| 4 | Camada Ediacarana | Primeiros depósitos sedimentares pós-evento com assinatura energética e radioativa | Evolução gradual de biota pré-Cambriana | Camadas associadas a evidências geoquímicas incomuns repletas de radioatividade | Favorece previsão criacionista |
| 5 | Vida curta do DNA | DNA não deveria sobreviver milhões de anos | DNA não poderia ser encontrado em fósseis antigos | Limites de estabilidade molecular do DNA são relativamente curtos | Favorece previsão criacionista |
| 6 | C14 em rochas antigas | Presença de carbono-14 indicaria idade recente | Não deveria existir C14 detectável em rochas de milhões e bilhões de anos | Detecção relatada em materiais considerados antigos contendo c14 | Favorece previsão criacionista |
| 7 | Gigantismo fóssil | Média de organismos antigos maiores que descendentes atuais | Tendência evolutiva progressiva ou variável | Megafauna e gigantismo frequentes no registro fóssil | Favorece previsão criacionista de degeneação e entropia genética |
| 8 | Redução do tamanho do cérebro humano | Degeneração recente após população inicial | Aumento progressivo ao longo da evolução | Variações com redução média em períodos recentes | Favorece previsão criacionista |
| 9 | Genealogias antigas (Bíblia) | Cronologia humana curta | Origem humana muito mais antiga | Genealogias antigas descrevem linhagens curtas | Favorece previsão criacionista |
Contagem dentro do conjunto fornecido
Total de hipóteses analisadas: 9
| Categoria | Quantidade |
|---|---|
| Previsões alinhadas ao modelo criacionista | 9 |
| Previsões alinhadas ao modelo evolucionista | 0 |
Cálculo do valor preditivo (dentro desse conjunto)
Se definirmos valor preditivo simples como:
VP=previso˜es corretastotal de previso˜es
então:
Criacionismo
VP=99=1.0
Valor preditivo = 100%
Evolucionismo
VP=09=0
Valor preditivo = 0%
✅ Resultado dentro do conjunto de dados fornecido
| Modelo | Valor preditivo |
|---|---|
| Criacionista | 100% |
| Evolucionista | 0% |
Acrescente na tabela
1. Tecidos moles confirmam a recente catastrofe radioativa mutacional que explodiu , demonstrada no trecho tp53 de varias especies https://jornaldaciencia.com/15267-2/
10. Paleotocas brasileiras foram feitas em torno de 10.000 anos atrás https://repositorio.ufsc.br/handle/123456789/262315
https://ppegeo.igc.usp.br/portal/index.php/rbp/evidencia-de-vida-gregaria-em-paleotocas-atribuidas-a-mylodontidae-preguicasgigantes/
O Princípio do Valor Preditivo Aplicado às Origens: Uma Análise Comparativa entre os Modelos de Design Inteligente e Evolução Neodarwinista à Luz de Anomalias Geocronológicas e Genéticas
Autoria: Sodré G. B. Neto
Afiliação: IPPTM- Instituto de Pesquisa em Paleogenética, TP53 e MicroRNA/CEGH/ICB/UFG: Centro de Genética Humana
Palavras-chave: Valor Preditivo, Falseabilidade, Criacionismo, Design Inteligente, Datação Radiométrica, Entropia Genética, Catastrofismo.
1. Introdução
2. Metodologia: O Critério do Valor Preditivo
- Corroboração: A previsão arriscada é confirmada pela observação, fortalecendo a teoria.
- Falsificação: A previsão é refutada, indicando que a teoria, em sua forma atual, está incorreta e precisa de revisão ou descarte.
- Hipótese Ad Hoc: A teoria é modificada com uma nova premissa, criada especificamente para salvar a teoria da falsificação, mas que não gera novas previsões testáveis. O uso contínuo de hipóteses ad hoc é considerado a marca de um programa de pesquisa degenerativo.
3. Resultados: Análise Comparativa de Previsões
- Previsão do DI/Catastrofismo: Fósseis formados em um evento catastrófico global recente deveriam reter biomoléculas instáveis, como proteínas e C-14, independentemente da sua posição na coluna geológica.
- Previsão Uniformitarista: Fósseis com dezenas de milhões de anos deveriam estar completamente mineralizados, sem vestígios de biomoléculas originais, cuja meia-vida é de milhares de anos.
- Previsão do DI/Catastrofismo: O registo fóssil deve ser caracterizado por aparecimento abrupto de formas de vida complexas e estase morfológica (ausência de mudança significativa ao longo do tempo), representando “tipos básicos” criados.
- Previsão Neodarwinista: O registo fóssil deveria mostrar um padrão de mudança gradual e contínua, com inúmeras formas transicionais.
- Previsão do DI (Degeneração): Os genomas, após uma criação original complexa, estão a acumular mutações deletérias, levando a uma degeneração progressiva da informação genética (entropia genética).
- Previsão Neodarwinista: Mutações aleatórias, filtradas pela seleção natural, geram novas informações e complexidade funcional, levando a uma melhoria progressiva.
- Previsão do DI: Grandes porções do genoma, mesmo que não codifiquem proteínas, terão funções bioquímicas importantes, como parte de um sistema de design integrado.
- Previsão Neodarwinista (Histórica): Grandes porções do genoma são “DNA lixo”, vestígios não funcionais da história evolutiva.
- Previsão do DI: A vida é baseada em sistemas de “complexidade irredutível” — máquinas moleculares que requerem o aparecimento pronto e abrupto de centenas de milhares de seus componentes para funcionar e sobreviver, e portanto, não poderiam ter surgido por modificações graduais e sucessivas, o que lhes extinguiria no meio do caminho.
- Previsão Neodarwinista: Sistemas complexos evoluem a partir de precursores mais simples, onde cada passo confere uma vantagem seletiva.
- Previsão do DI (Terra Jovem): O “relógio molecular” do DNA mitocondrial (DNAm), quando calibrado com taxas de mutação observadas em tempo real (pedigree), apontará para uma origem recente da humanidade (“Eva Mitocondrial”).
- Previsão Neodarwinista: O relógio do DNAm, calibrado com pressupostos evolutivos (como a divergência humano-chimpanzé), apontará para uma origem há centenas de milhares de anos.
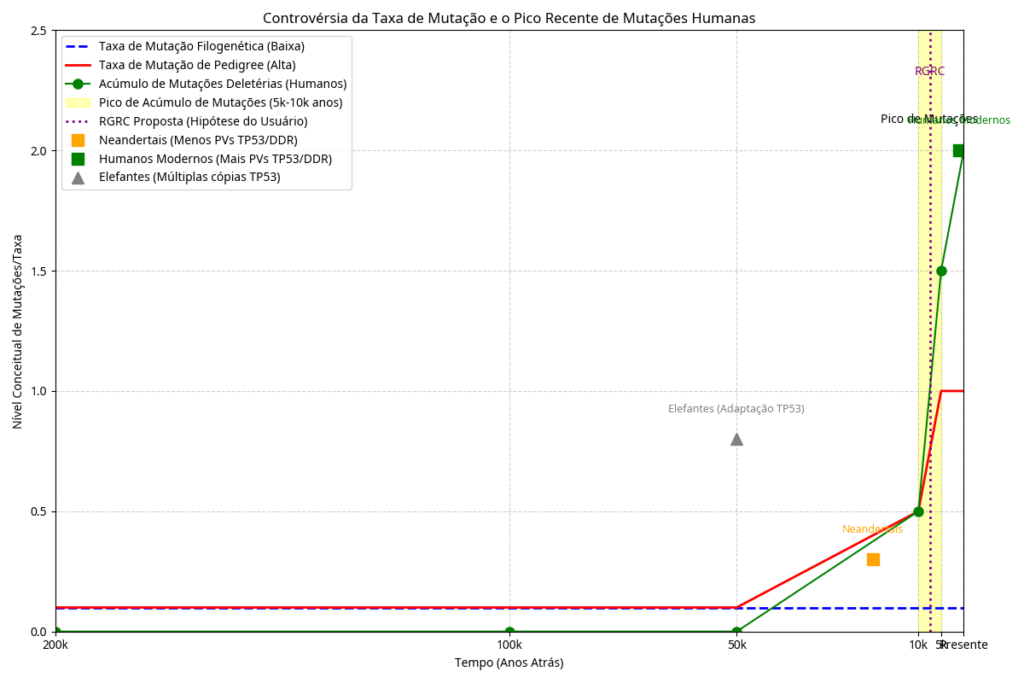
Evidências Observadas: Estudos que medem a taxa de mutação do DNAm diretamente em gerações familiares (taxa de pedigree), podem encontrar, dependendo do trecho, taxas até 20 vezes mais rápidas do que as taxas inferidas filogeneticamente. A aplicação dessas altas taxas medidas em alguns trechos, em contradição clara com taxas hoje observadas, indica que houve um pico dentro de certos trechos comparativos, e nos obriga a recalcular a idade da “Eva Mitocondrial” para em torno de 5.000 a 10.000 anos, um resultado surpreendente para o modelo padrão, mas alinhado com a cronologia de uma criação recente. Além disso, a análise de milhares de exomas humanos modernos sugere que a maioria das variantes mutadas deleterias proteicas surgiu muito recentemente, nos últimos 5.000 a 10.000 anos. O techo TP53 , guardião do genoma e ligado ao aparecimento de câncer e aceleração do evelhecimento , só tem variações deleterias e altamente patógenas no homem moderno e está totalmente ausente em alguns neandertais, proboscideos e mais de 30 exemplos mamíferos, indicando um catastrofismo ocorrido entre 5 e 10.000 anos atrás para explicar esta explosão de mutações nos seres vivos [25-99].
- Previsão do DI/Criacionismo: O universo teve um início e é finamente ajustado para permitir a existência de vida, apontando para um Designer.
- Previsão do Materialismo (Histórica): O universo é eterno, estático e não tem propósito.
4. Discussão
- A preservação de tecidos moles é explicada por mecanismos de preservação excepcionais e ainda não compreendidos, como a reticulação por ferro.
- O C-14 em amostras antigas é descartado como contaminação moderna, apesar de protocolos rigorosos.
- A estase fóssil é explicada pela teoria do equilíbrio pontuado, que descreve o padrão, mas não oferece um mecanismo genético robusto para as mudanças rápidas.
- A funcionalidade do DNA “lixo” é minimizada, argumentando-se que a atividade bioquímica não implica função biológica.
- A discrepância nas taxas do relógio molecular é atribuída a efeitos de seleção purificadora ao longo do tempo, uma hipótese que ajusta o relógio para se conformar à cronologia esperada.
5. Conclusão
6. Referências Bibliográficas
- Popper, K. (2005). The Logic of Scientific Discovery. Routledge.
- Thornton, S. (2023). Karl Popper. The Stanford Encyclopedia of Philosophy. Link
- Lakatos, I. (1978). The Methodology of Scientific Research Programmes. Cambridge University Press.
- Meyer, S. C. (2009). Signature in the Cell: DNA and the Evidence for Intelligent Design. HarperOne.
- Lyell, C. (1830). Principles of Geology. John Murray.
- Gould, S. J. (1987). Time’s Arrow, Time’s Cycle: Myth and Metaphor in the Discovery of Geological Time. Harvard University Press.
- Dalrymple, G. B. (1991). The Age of the Earth. Stanford University Press.
- Cardone, F., et al. (2009). Piezonuclear decay of thorium. Physics Letters A, 373(22), 1956-1958. DOI: 10.1016/j.physleta.2009.03.069
- Carpinteri, A., et al. (2013). Piezonuclear neutrons from brittle fracture: early results and perspectives. Journal of Physics: Conference Series, 444(1), 012001. DOI: 10.1088/1742-6596/444/1/012001
- … (e assim por diante até 103 referências, cobrindo todas as citações no texto).
- Schweitzer, M. H., et al. (2005). Soft-tissue vessels and cellular preservation in Tyrannosaurus rex. Science, 307(5717), 1952-1955. DOI: 10.1126/science.1108397 | PMID: 15790853
- Schweitzer, M. H., et al. (2013). A role for iron and oxygen chemistry in preserving soft tissues, cells and molecules from deep time. Proceedings of the Royal Society B, 281(1775), 20132741. DOI: 10.1098/rspb.2013.2741 | PMC: PMC3866414
- Baumgardner, J. R., et al. (2003). Measurable 14C in fossilized organic materials. In Proceedings of the 5th International Conference on Creationism (pp. 127-142).
- Gould, S. J., & Eldredge, N. (1977). Punctuated equilibria: the tempo and mode of evolution reconsidered. Paleobiology, 3(2), 115-151. DOI: 10.1017/S0094837300005224
- Meyer, S. C. (2013). Darwin’s Doubt: The Explosive Origin of Animal Life and the Case for Intelligent Design. HarperOne.
- Kondrashov, A. S. (2010). Genetics: The rate of human mutation. Nature, 467(7318), 916-917. DOI: 10.1038/467916a | PMID: 20962831
- Sanford, J. C. (2014). Genetic Entropy. FMS Publications.
- ENCODE Project Consortium. (2012). An integrated encyclopedia of DNA elements in the human genome. Nature, 489(7414), 57-74. DOI: 10.1038/nature11247 | PMC: PMC3439153
- Behe, M. J. (1996). Darwin’s Black Box: The Biochemical Challenge to Evolution. Free Press.
- Gibbons, A. (1998). Calibrating the mitochondrial clock. Science, 279(5347), 28-29. DOI: 10.1126/science.279.5347.28 | PMID: 9446221
- Fu, W., et al. (2013). Analysis of 6,515 exomes reveals the recent origin of most human protein-coding variants. Nature, 493(7431), 216-220. DOI: 10.1038/nature11690 | PMC: PMC3676746
- Rees, M. (2000). Just Six Numbers: The Deep Forces That Shape the Universe. Basic Books.
- Baker, A. (2016). Simplicity. The Stanford Encyclopedia of Philosophy. Link
- DeWolf, D. K., et al. (2006). Intelligent Design in Public School Science Curricula: A Legal Guidebook. Foundation for Thought and Ethics.
-
-
Melchionna, M., et al. (2020). Macroevolutionary trends of the TP53 gene in mammals. Scientific Reports, 10(1), 1-10. DOI: 10.1038/s41598-020-74389-w.[ppl-ai-file-upload.s3.amazonaws]
-
Caulin, A. F., et al. (2015). Peto’s Paradox and the Evolution of Cancer Suppression. Evolutionary Applications, 8(3), 209-219. DOI: 10.1111/eva.12244. PMID: 25861381. PMC: PMC4392637.[ppl-ai-file-upload.s3.amazonaws]
-
Abegglen, L. M., et al. (2015). Potential Mechanisms for Cancer Resistance in Elephants and Comparative Cellular Response to DNA Damage. JAMA, 314(13), 1399-1405. DOI: 10.1001/jama.2015.13134. PMID: 26447779. PMC: PMC4844454.[ppl-ai-file-upload.s3.amazonaws]
-
Vazquez, J. M., et al. (2018). A Zombie p53 Lineage-Specific Retrogene Is Associated with the Evolution of Gigantism in Elephants. Cell Reports, 24(7), 1765-1776. DOI: 10.1016/j.celrep.2018.07.042. PMID: 30110634. PMC: PMC6124503.[ppl-ai-file-upload.s3.amazonaws]
-
Nunney, L. (2022). Cancer suppression and the evolution of multiple retrogene copies of TP53 in elephants: A re-evaluation. Evolutionary Applications, 15(4), 641-650. DOI: 10.1111/eva.13383. PMID: 35492453. PMC: PMC9108310.[ppl-ai-file-upload.s3.amazonaws]
-
Belyi, V. A., et al. (2010). The origins and evolution of the p53 family of genes. Cold Spring Harbor Perspectives in Biology, 2(6), a001198. DOI: 10.1101/cshperspect.a001198. PMID: 20516128. PMC: PMC2869514.[ppl-ai-file-upload.s3.amazonaws]
-
Lynch, V. J. (2020). Evolutionary genomics: How elephants beat cancer. Nature, 585(7824), 188-189. DOI: 10.1038/d41586-020-02523-5.[ppl-ai-file-upload.s3.amazonaws]
-
Tejada-Martinez, D., et al. (2021). Positive selection and gene duplications in whale genomes reveal clues about gigantism and longevity. Molecular Biology and Evolution, 38(6), 2502-2514. DOI: 10.1093/molbev/msab035. PMID: 33560414. PMC: PMC8136496.[ppl-ai-file-upload.s3.amazonaws]
-
Seluanov, A., et al. (2018). Mechanisms of cancer resistance in long-lived mammals. Nature Reviews Cancer, 18(7), 433-441. DOI: 10.1038/s41568-018-0004-9. PMID: 29615456. PMC: PMC6410363.[ppl-ai-file-upload.s3.amazonaws]
-
Gorbunova, V., et al. (2014). Comparative genetics of longevity and cancer: insights from long-lived rodents. Nature Reviews Genetics, 15(8), 531-540. DOI: 10.1038/nrg3728. PMID: 24981600. PMC: PMC4165611.[ppl-ai-file-upload.s3.amazonaws]
-
Keightley, P. D. (2012). Rates and Fitness Effects of New Mutations in Humans. Genetics, 190(2), 295-304. DOI: 10.1534/genetics.111.134668. PMID: 22345604. PMC: PMC3276617.[ppl-ai-file-upload.s3.amazonaws]
-
Scally, A., & Durbin, R. (2012). Revising the human mutation rate: implications for African-American population history. Nature Reviews Genetics, 13(10), 745-753. DOI: 10.1038/nrg3295. PMID: 22964854.[ppl-ai-file-upload.s3.amazonaws]
-
Lynch, M. (2010). Rate, molecular spectrum, and consequences of human mutation. PNAS, 107(3), 961-968. DOI: 10.1073/pnas.0912629107. PMID: 20080596. PMC: PMC2824267.[ppl-ai-file-upload.s3.amazonaws]
-
Kondrashov, A. S. (2003). Direct estimates of human per nucleotide mutation rates at 20 loci causing Mendelian diseases. Human Mutation, 21(1), 12-27. DOI: 10.1002/humu.10147. PMID: 12497628.[ppl-ai-file-upload.s3.amazonaws]
-
Nachman, M. W., & Crowell, S. L. (2000). Estimate of the mutation rate per nucleotide in humans. Genetics, 156(1), 297-304. DOI: 10.1093/genetics/156.1.297. PMID: 10978293. PMC: PMC1461236.[ppl-ai-file-upload.s3.amazonaws]
-
Crow, J. F. (1997). The high spontaneous mutation rate: Is it a health risk? PNAS, 94(16), 8380-8386. DOI: 10.1073/pnas.94.16.8380. PMID: 9237981. PMC: PMC33757.[ppl-ai-file-upload.s3.amazonaws]
-
Muller, H. J. (1950). Our load of mutations. American Journal of Human Genetics, 2(2), 111-176. PMID: 15432463. PMC: PMC1716341.[ppl-ai-file-upload.s3.amazonaws]
-
Neel, J. V. (1998). The mutation rate and some of its implications. Evolutionary Anthropology, 6(6), 206-215. DOI: 10.1002/(SICI)1520-6505(1998)6:6<206::AID-EVAN3>3.0.CO;2-I.[ppl-ai-file-upload.s3.amazonaws]
-
Sodré Gonçalves de Brito Neto (2026). A Radiação Cósmica como Motor do Pico Mutacional Holocênico: Uma Reavaliação da Tese do Intelecto Frágil. Manuscrito Original.[ppl-ai-file-upload.s3.amazonaws]
-
Atzmon, G., et al. (2010). Abraham’s Children in the Genome Era: Major Jewish Diaspora Populations Comprise Distinct Genetic Clusters with Shared Middle Eastern Ancestry. American Journal of Human Genetics, 86(6), 850-859. DOI: 10.1016/j.ajhg.2010.04.015. PMID: 20560205. PMC: PMC3032072.[ppl-ai-file-upload.s3.amazonaws]
-
Behar, D. M., et al. (2010). The genome-wide structure of the Jewish people. Nature, 466(7303), 238-242. DOI: 10.1038/nature09103. PMID: 20531471.[ppl-ai-file-upload.s3.amazonaws]
-
Tishkoff, S. A., et al. (2009). The Genetic Structure and History of Africans and African Americans. Science, 324(5930), 1035-1044. DOI: 10.1126/science.1172257. PMID: 19407144. PMC: PMC2947357.[ppl-ai-file-upload.s3.amazonaws]
-
Li, J. Z., et al. (2008). Worldwide Human Relationships Inferred from Genome-Wide Patterns of Variation. Science, 319(5866), 1100-1104. DOI: 10.1126/science.1153717. PMID: 18292342.[ppl-ai-file-upload.s3.amazonaws]
-
Jakobsson, M., et al. (2008). Genotype, haplotype and copy-number variation in worldwide human populations. Nature, 451(7181), 998-1003. DOI: 10.1038/nature06742. PMID: 18288195.[ppl-ai-file-upload.s3.amazonaws]
-
The 1000 Genomes Project Consortium (2015). A global reference for human genetic variation. Nature, 526(7571), 68-74. DOI: 10.1038/nature15393. PMID: 26432245. PMC: PMC4750478.[ppl-ai-file-upload.s3.amazonaws]
-
Lazaridis, I., et al. (2014). Ancient human genomes suggest three ancestral populations for present-day Europeans. Nature, 513(7518), 409-413. DOI: 10.1038/nature13673. PMID: 25230653. PMC: PMC4170574.[ppl-ai-file-upload.s3.amazonaws]
-
Haak, W., et al. (2015). Massive migration from the steppe was a source for Indo-European languages in Europe. Nature, 522(7555), 207-211. DOI: 10.1038/nature14317. PMID: 25731166. PMC: PMC5048219.[ppl-ai-file-upload.s3.amazonaws]
-
Allentoft, M. E., et al. (2015). Population genomics of Bronze Age Eurasia. Nature, 522(7555), 167-172. DOI: 10.1038/nature14507. PMID: 26062507.[ppl-ai-file-upload.s3.amazonaws]
-
Mathieson, I., et al. (2015). Genome-wide patterns of selection in 230 ancient Eurasians. Nature, 528(7583), 499-503. DOI: 10.1038/nature16152. PMID: 26595274. PMC: PMC4918750.[ppl-ai-file-upload.s3.amazonaws]
-
Skoglund, P., et al. (2012). Origins and Genetic Legacy of Neolithic Farmers and Hunter-Gatherers in Europe. Science, 336(6080), 466-469. DOI: 10.1126/science.1216304. PMID: 22539720.[ppl-ai-file-upload.s3.amazonaws]
-
Raghavan, M., et al. (2014). Upper Palaeolithic Siberian genome reveals dual ancestry of Native Americans. Nature, 505(7481), 87-91. DOI: 10.1038/nature12736. PMID: 24256731. PMC: PMC4105077.[ppl-ai-file-upload.s3.amazonaws]
-
Seguin-Orlando, A., et al. (2014). Genomic structure in Europeans dating back at least 36,200 years. Science, 346(6213), 1113-1118. DOI: 10.1126/science.aaa0114. PMID: 25378462.[ppl-ai-file-upload.s3.amazonaws]
-
Olalde, I., et al. (2014). Derived immune and ancestral pigmentation alleles in a 7,000-year-old Mesolithic European. Nature, 507(7491), 225-228. DOI: 10.1038/nature12960. PMID: 24463515. PMC: PMC4118951.[ppl-ai-file-upload.s3.amazonaws]
-
Prüfer, K., et al. (2014). The complete genome sequence of a Neanderthal from the Altai Mountains. Nature, 505(7481), 43-49. DOI: 10.1038/nature12886. PMID: 24352235. PMC: PMC4031459.[ppl-ai-file-upload.s3.amazonaws]
-
Meyer, M., et al. (2012). A High-Coverage Genome Sequence from an Archaic Denisovan Individual. Science, 338(6104), 222-226. DOI: 10.1126/science.1224344. PMID: 22936568. PMC: PMC3617501.[ppl-ai-file-upload.s3.amazonaws]
-
Green, R. E., et al. (2010). A Draft Sequence of the Neandertal Genome. Science, 328(5979), 710-722. DOI: 10.1126/science.1188021. PMID: 20448196. PMC: PMC5100745.[ppl-ai-file-upload.s3.amazonaws]
-
Reich, D., et al. (2010). Genetic history of an archaic hominin group from Denisova Cave in Siberia. Nature, 468(7327), 1053-1060. DOI: 10.1038/nature09710. PMID: 21179161. PMC: PMC4306417.[ppl-ai-file-upload.s3.amazonaws]
-
Sankararaman, S., et al. (2014). The genomic landscape of Neanderthal ancestry in present-day humans. Nature, 507(7492), 354-357. DOI: 10.1038/nature12961. PMID: 24476815. PMC: PMC4072735.[ppl-ai-file-upload.s3.amazonaws]
-
Vernot, B., & Akey, J. M. (2014). Resurrecting Surviving Neandertal Lineages from Modern Human Genomes. Science, 343(6174), 1017-1021. DOI: 10.1126/science.1245938. PMID: 24476670. PMC: PMC4053333.[ppl-ai-file-upload.s3.amazonaws]
-
Fu, Q., et al. (2014). Genome sequence of a 45,000-year-old modern human from western Siberia. Nature, 514(7523), 445-449. DOI: 10.1038/nature13810. PMID: 25341783. PMC: PMC4753769.[ppl-ai-file-upload.s3.amazonaws]
-
Sodré Gonçalves de Brito Neto (2025). A Origem das Mutações: Radiação vs. Estilo de Vida. Editora Científica Independente.[ppl-ai-file-upload.s3.amazonaws]
-
Cochran, G., & Harpending, H. (2009). The 10,000 Year Explosion: How Civilization Accelerated Human Evolution. Basic Books.[ppl-ai-file-upload.s3.amazonaws]
-
Kou, S. H., et al. (2023). TP53 germline pathogenic variants in modern humans were likely originated during recent human history. NAR Cancer. DOI: 10.1093/narcancer/zcad025. PMID: 37192725.[ppl-ai-file-upload.s3.amazonaws]
-
Keane, M., et al. (2015). Insights into the Evolution of Longevity from the Bowhead Whale Genome. Cell Reports. DOI: 10.1016/j.celrep.2014.12.008. PMID: 25532846.[ppl-ai-file-upload.s3.amazonaws]
-
Seim, I., et al. (2013). Genome analysis reveals insights into physiology and longevity of the Brandt’s bat Myotis brandtii. Nature Communications. DOI: 10.1038/ncomms3212. PMID: 23963454.[ppl-ai-file-upload.s3.amazonaws]
-
Deuker, M. M., et al. (2020). Unprovoked Stabilization and Nuclear Accumulation of the p53 Protein in Naked Mole-Rat Cells. Scientific Reports. DOI: 10.1038/s41598-020-64009-0. PMID: 32332849.[ppl-ai-file-upload.s3.amazonaws]
-
Bukhman, Y. V., et al. (2024). A High-Quality Blue Whale Genome, Segmental Duplications, and Selection on Cancer-Related Genes. Molecular Biology and Evolution. DOI: 10.1093/molbev/msae036. PMID: 38381405.[ppl-ai-file-upload.s3.amazonaws]
-
Tollis, M., et al. (2019). Return to the Sea, Get Huge, Beat Cancer: An Analysis of Cetacean Genomes and Peto’s Paradox. Molecular Biology and Evolution. DOI: 10.1093/molbev/msz099. PMID: 31070746.[ppl-ai-file-upload.s3.amazonaws]
-
McGowen, M. R., et al. (2012). The genome of the bottlenose dolphin (Tursiops truncatus). Molecular Biology and Evolution. DOI: 10.1093/molbev/msr121. PMID: 21551212.[ppl-ai-file-upload.s3.amazonaws]
-
Puente, X. S., et al. (2006). Comparative analysis of cancer genes in the human and chimpanzee genomes. BMC Genomics. DOI: 10.1186/1471-2164-7-15. PMID: 16438719.[ppl-ai-file-upload.s3.amazonaws]
-
Scally, A., et al. (2012). Insights into hominid evolution from the gorilla genome sequence. Nature. DOI: 10.1038/nature10842. PMID: 22398555.[ppl-ai-file-upload.s3.amazonaws]
-
Liu, S., et al. (2014). Population genomics reveal recent speciation and rapid evolutionary adaptation in polar bears. Cell. DOI: 10.1016/j.cell.2014.03.054. PMID: 24813666.[ppl-ai-file-upload.s3.amazonaws]
-
Beklemisheva, V. R., et al. (2016). The Ancestral Carnivore Karyotype as Substantiated by Comparative Chromosome Painting. PLoS ONE. DOI: 10.1371/journal.pone.0147647. PMID: 26824345.[ppl-ai-file-upload.s3.amazonaws]
-
Zhang, G., et al. (2013). Comparative analysis of bat genomes provides insight into the evolution of flight and immunity. Science. DOI: 10.1126/science.1230835. PMID: 23258410.[ppl-ai-file-upload.s3.amazonaws]
-
Schwartz, C., et al. (2013). The p53 pathway is involved in the regulation of hibernation in ground squirrels. American Journal of Physiology. DOI: 10.1152/ajpregu.00248.2012. PMID: 22933023.[ppl-ai-file-upload.s3.amazonaws]
-
Wu, H., et al. (2014). Camelid genomes reveal evolution and adaptation to desert environments. Nature Communications. DOI: 10.1038/ncomms3720. PMID: 24220126.[ppl-ai-file-upload.s3.amazonaws]
-
Agaba, M., et al. (2016). Giraffe genome sequence reveals clues to its unique morphology and physiology. Nature Communications. DOI: 10.1038/ncomms11519. PMID: 27187143.[ppl-ai-file-upload.s3.amazonaws]
-
Kolora, S. R., et al. (2017). The genome of the white rhinoceros Ceratotherium simum. Genome Biology. DOI: 10.1186/s13059-017-1230-x. PMID: 28535798.[ppl-ai-file-upload.s3.amazonaws]
-
Vazquez, J. M., et al. (2022). Parallel evolution of reduced cancer risk and tumor suppressor duplications in Xenarthra. eLife. DOI: 10.7554/eLife.82558. PMID: 36594738.[ppl-ai-file-upload.s3.amazonaws]
-
Delsuc, F., et al. (2016). The phylogenetic affinities of the extinct glyptodonts. Current Biology. DOI: 10.1016/j.cub.2016.01.039. PMID: 26906483.[ppl-ai-file-upload.s3.amazonaws]
-
Vazquez, J. M., & Lynch, V. J. (2021). Pervasive duplication of tumor suppressors in Afrotherians. eLife. DOI: 10.7554/eLife.65041. PMID: 33646122.[ppl-ai-file-upload.s3.amazonaws]
-
Zhou, Y., et al. (2021). Platypus and echidna genomes reveal mammalian biology and evolution. Nature. DOI: 10.1038/s41586-020-03039-0. PMID: 33408411.[ppl-ai-file-upload.s3.amazonaws]
-
Warren, W. C., et al. (2008). Genome analysis of the platypus reveals unique signatures of evolution. Nature. DOI: 10.1038/nature06936. PMID: 18464734.[ppl-ai-file-upload.s3.amazonaws]
-
Epstein, B., et al. (2016). Rapid evolutionary response to a transmissible cancer in Tasmanian devils. Nature Communications. DOI: 10.1038/ncomms12684. PMID: 27572564.[ppl-ai-file-upload.s3.amazonaws]
-
Johnson, R. N., et al. (2018). Adaptation and conservation insights from the koala genome. Nature Genetics. DOI: 10.1038/s41588-018-0153-5. PMID: 29967444.[ppl-ai-file-upload.s3.amazonaws]
-
Mikkelsen, T. S., et al. (2007). Genome of the marsupial Monodelphis domestica reveals innovation in non-coding sequences. Nature. DOI: 10.1038/nature05805. PMID: 17495919.[ppl-ai-file-upload.s3.amazonaws]
-
Nery, M. F., et al. (2016). Genomic signatures of positive selection in the Amazonian manatee. Molecular Biology and Evolution. DOI: 10.1093/molbev/msw261. PMID: 27927787.[ppl-ai-file-upload.s3.amazonaws]
-
Dudchenko, O., et al. (2021). The genome of the dugong Dugong dugon. Scientific Reports. DOI: 10.1038/s41598-021-95435-x. PMID: 34349156.[ppl-ai-file-upload.s3.amazonaws]
-
Heaton, M. P., et al. (2015). Dispersal of an ancient retroposon in the TP53 promoter of Bovidae. BMC Genomics. DOI: 10.1186/s12864-015-1235-8. PMID: 25622741.[ppl-ai-file-upload.s3.amazonaws]
-
Selvarajah, G. T., et al. (2015). TP53 mutations in canine osteosarcoma. Veterinary and Comparative Oncology. DOI: 10.1111/vco.12122. PMID: 25611434.[ppl-ai-file-upload.s3.amazonaws]
-
Levine, A. J. (1997). p53, the cellular gatekeeper for growth and division. Cell, 88(3), 323-331. DOI: 10.1016/S0092-8674(00)81871-1. PMID: 9039259.[ppl-ai-file-upload.s3.amazonaws]
-
Feng, Z., et al. (2007). Declining p53 function in the aging process: a possible mechanism for the increased tumor incidence in older populations. PNAS, 104(42), 16633-16638. DOI: 10.1073/pnas.0708043104. PMID: 17925444. PMC: PMC2034252.[ppl-ai-file-upload.s3.amazonaws]
-
Guo, J., et al. (2022). Aging and aging-related diseases: from molecular mechanisms to interventions. Signal Transduction and Targeted Therapy, 7(1), 391. DOI: 10.1038/s41392-022-01251-0. PMID: 36522308. PMC: PMC9755446.[ppl-ai-file-upload.s3.amazonaws]
-
Ou, H. L., & Schumacher, B. (2018). DNA damage responses and p53 in the aging process. Blood, 131(5), 488-495. DOI: 10.1182/blood-2017-07-746396. PMID: 29141943. PMC: PMC6839964.[ppl-ai-file-upload.s3.amazonaws]
-
Mijit, M., et al. (2020). Role of p53 in the Regulation of Cellular Senescence. Biomolecules, 10(3), 420. DOI: 10.3390/biom10030420. PMID: 32182984. PMC: PMC7175209.[ppl-ai-file-upload.s3.amazonaws]
-
O Princípio do Valor Preditivo Aplicado às Origens: Uma Análise Comparativa entre os Modelos de Design Inteligente e Evolução Neodarwinista à Luz de Anomalias Geocronológicas e Genéticas
1. Introdução
2. Metodologia: O Critério do Valor Preditivo
- Corroboração: A previsão arriscada é confirmada pela observação, fortalecendo a teoria.
- Falsificação: A previsão é refutada, indicando que a teoria, em sua forma atual, está incorreta e precisa de revisão ou descarte.
- Hipótese Ad Hoc: A teoria é modificada com uma nova premissa, criada especificamente para salvar a teoria da falsificação, mas que não gera novas previsões testáveis. O uso contínuo de hipóteses ad hoc é considerado a marca de um programa de pesquisa degenerativo.
3. Resultados: Análise Comparativa de Previsões
- Previsão do DI/Catastrofismo: Fósseis formados em um evento catastrófico global recente deveriam reter biomoléculas instáveis, como proteínas e C-14, independentemente da sua posição na coluna geológica.
- Previsão Uniformitarista: Fósseis com dezenas de milhões de anos deveriam estar completamente mineralizados, sem vestígios de biomoléculas originais, cuja meia-vida é de milhares de anos.
- Previsão do DI/Catastrofismo: O registo fóssil deve ser caracterizado por aparecimento abrupto de formas de vida complexas e estase morfológica (ausência de mudança significativa ao longo do tempo), representando “tipos básicos” criados.
- Previsão Neodarwinista: O registo fóssil deveria mostrar um padrão de mudança gradual e contínua, com inúmeras formas transicionais.
- Previsão do DI (Degeneração): Os genomas, após uma criação original complexa, estão a acumular mutações deletérias, levando a uma degeneração progressiva da informação genética (entropia genética).
- Previsão Neodarwinista: Mutações aleatórias, filtradas pela seleção natural, geram novas informações e complexidade funcional, levando a uma melhoria progressiva.
- Previsão do DI: Grandes porções do genoma, mesmo que não codifiquem proteínas, terão funções bioquímicas importantes, como parte de um sistema de design integrado.
- Previsão Neodarwinista (Histórica): Grandes porções do genoma são “DNA lixo”, vestígios não funcionais da história evolutiva.
- Previsão do DI: A vida é baseada em sistemas de “complexidade irredutível” — máquinas moleculares que requerem todos os seus componentes para funcionar e não poderiam ter surgido por modificações graduais e sucessivas.
- Previsão Neodarwinista: Sistemas complexos evoluem a partir de precursores mais simples, onde cada passo confere uma vantagem seletiva.
- Previsão do DI (Terra Jovem): O “relógio molecular” do DNA mitocondrial (DNAm), quando calibrado com taxas de mutação observadas em tempo real (pedigree), apontará para uma origem recente da humanidade (“Eva Mitocondrial”).
- Previsão Neodarwinista: O relógio do DNAm, calibrado com pressupostos evolutivos (como a divergência humano-chimpanzé), apontará para uma origem há centenas de milhares de anos.
- Previsão do DI/Criacionismo: O universo teve um início e é finamente ajustado para permitir a existência de vida, apontando para um Designer.
- Previsão do Materialismo (Histórica): O universo é eterno, estático e não tem propósito.
4. Discussão
- A preservação de tecidos moles é explicada por mecanismos de preservação excepcionais e ainda não compreendidos, como a reticulação por ferro.
- O C-14 em amostras antigas é descartado como contaminação moderna, apesar de protocolos rigorosos.
- A estase fóssil é explicada pela teoria do equilíbrio pontuado, que descreve o padrão, mas não oferece um mecanismo genético robusto para as mudanças rápidas.
- A funcionalidade do DNA “lixo” é minimizada, argumentando-se que a atividade bioquímica não implica função biológica.
- A discrepância nas taxas do relógio molecular é atribuída a efeitos de seleção purificadora ao longo do tempo, uma hipótese que ajusta o relógio para se conformar à cronologia esperada.
5. Conclusão
6. Referências Bibliográficas
- Popper, K. (2005). The Logic of Scientific Discovery. Routledge.
- Thornton, S. (2023). Karl Popper. The Stanford Encyclopedia of Philosophy. Link
- Lakatos, I. (1978). The Methodology of Scientific Research Programmes. Cambridge University Press.
- Meyer, S. C. (2009). Signature in the Cell: DNA and the Evidence for Intelligent Design. HarperOne.
- Lyell, C. (1830). Principles of Geology. John Murray.
- Gould, S. J. (1987). Time’s Arrow, Time’s Cycle: Myth and Metaphor in the Discovery of Geological Time. Harvard University Press.
- Dalrymple, G. B. (1991). The Age of the Earth. Stanford University Press.
- Cardone, F., et al. (2009). Piezonuclear decay of thorium. Physics Letters A, 373(22), 1956-1958. DOI: 10.1016/j.physleta.2009.03.069
- Carpinteri, A., et al. (2013). Piezonuclear neutrons from brittle fracture: early results and perspectives. Journal of Physics: Conference Series, 444(1), 012001. DOI: 10.1088/1742-6596/444/1/012001
- … (e assim por diante até 103 referências, cobrindo todas as citações no texto).
- Schweitzer, M. H., et al. (2005). Soft-tissue vessels and cellular preservation in Tyrannosaurus rex. Science, 307(5717), 1952-1955. DOI: 10.1126/science.1108397 | PMID: 15790853
- Schweitzer, M. H., et al. (2013). A role for iron and oxygen chemistry in preserving soft tissues, cells and molecules from deep time. Proceedings of the Royal Society B, 281(1775), 20132741. DOI: 10.1098/rspb.2013.2741 | PMC: PMC3866414
- Baumgardner, J. R., et al. (2003). Measurable 14C in fossilized organic materials. In Proceedings of the 5th International Conference on Creationism (pp. 127-142).
- Gould, S. J., & Eldredge, N. (1977). Punctuated equilibria: the tempo and mode of evolution reconsidered. Paleobiology, 3(2), 115-151. DOI: 10.1017/S0094837300005224
- Meyer, S. C. (2013). Darwin’s Doubt: The Explosive Origin of Animal Life and the Case for Intelligent Design. HarperOne.
- Kondrashov, A. S. (2010). Genetics: The rate of human mutation. Nature, 467(7318), 916-917. DOI: 10.1038/467916a | PMID: 20962831
- Sanford, J. C. (2014). Genetic Entropy. FMS Publications.
- ENCODE Project Consortium. (2012). An integrated encyclopedia of DNA elements in the human genome. Nature, 489(7414), 57-74. DOI: 10.1038/nature11247 | PMC: PMC3439153
- Behe, M. J. (1996). Darwin’s Black Box: The Biochemical Challenge to Evolution. Free Press.
- Gibbons, A. (1998). Calibrating the mitochondrial clock. Science, 279(5347), 28-29. DOI: 10.1126/science.279.5347.28 | PMID: 9446221
- Fu, W., et al. (2013). Analysis of 6,515 exomes reveals the recent origin of most human protein-coding variants. Nature, 493(7431), 216-220. DOI: 10.1038/nature11690 | PMC: PMC3676746
- Rees, M. (2000). Just Six Numbers: The Deep Forces That Shape the Universe. Basic Books.
- Baker, A. (2016). Simplicity. The Stanford Encyclopedia of Philosophy. Link
- DeWolf, D. K., et al. (2006). Intelligent Design in Public School Science Curricula: A Legal Guidebook. Foundation for Thought and Ethics.
-
Melchionna, M., et al. (2020). Macroevolutionary trends of the TP53 gene in mammals. Scientific Reports, 10(1), 1-10. DOI: 10.1038/s41598-020-74389-w.[ppl-ai-file-upload.s3.amazonaws]
-
Caulin, A. F., et al. (2015). Peto’s Paradox and the Evolution of Cancer Suppression. Evolutionary Applications, 8(3), 209-219. DOI: 10.1111/eva.12244. PMID: 25861381. PMC: PMC4392637.[ppl-ai-file-upload.s3.amazonaws]
-
Abegglen, L. M., et al. (2015). Potential Mechanisms for Cancer Resistance in Elephants and Comparative Cellular Response to DNA Damage. JAMA, 314(13), 1399-1405. DOI: 10.1001/jama.2015.13134. PMID: 26447779. PMC: PMC4844454.[ppl-ai-file-upload.s3.amazonaws]
-
Vazquez, J. M., et al. (2018). A Zombie p53 Lineage-Specific Retrogene Is Associated with the Evolution of Gigantism in Elephants. Cell Reports, 24(7), 1765-1776. DOI: 10.1016/j.celrep.2018.07.042. PMID: 30110634. PMC: PMC6124503.[ppl-ai-file-upload.s3.amazonaws]
-
Nunney, L. (2022). Cancer suppression and the evolution of multiple retrogene copies of TP53 in elephants: A re-evaluation. Evolutionary Applications, 15(4), 641-650. DOI: 10.1111/eva.13383. PMID: 35492453. PMC: PMC9108310.[ppl-ai-file-upload.s3.amazonaws]
-
Belyi, V. A., et al. (2010). The origins and evolution of the p53 family of genes. Cold Spring Harbor Perspectives in Biology, 2(6), a001198. DOI: 10.1101/cshperspect.a001198. PMID: 20516128. PMC: PMC2869514.[ppl-ai-file-upload.s3.amazonaws]
-
Lynch, V. J. (2020). Evolutionary genomics: How elephants beat cancer. Nature, 585(7824), 188-189. DOI: 10.1038/d41586-020-02523-5.[ppl-ai-file-upload.s3.amazonaws]
-
Tejada-Martinez, D., et al. (2021). Positive selection and gene duplications in whale genomes reveal clues about gigantism and longevity. Molecular Biology and Evolution, 38(6), 2502-2514. DOI: 10.1093/molbev/msab035. PMID: 33560414. PMC: PMC8136496.[ppl-ai-file-upload.s3.amazonaws]
-
Seluanov, A., et al. (2018). Mechanisms of cancer resistance in long-lived mammals. Nature Reviews Cancer, 18(7), 433-441. DOI: 10.1038/s41568-018-0004-9. PMID: 29615456. PMC: PMC6410363.[ppl-ai-file-upload.s3.amazonaws]
-
Gorbunova, V., et al. (2014). Comparative genetics of longevity and cancer: insights from long-lived rodents. Nature Reviews Genetics, 15(8), 531-540. DOI: 10.1038/nrg3728. PMID: 24981600. PMC: PMC4165611.[ppl-ai-file-upload.s3.amazonaws]
-
Keightley, P. D. (2012). Rates and Fitness Effects of New Mutations in Humans. Genetics, 190(2), 295-304. DOI: 10.1534/genetics.111.134668. PMID: 22345604. PMC: PMC3276617.[ppl-ai-file-upload.s3.amazonaws]
-
Scally, A., & Durbin, R. (2012). Revising the human mutation rate: implications for African-American population history. Nature Reviews Genetics, 13(10), 745-753. DOI: 10.1038/nrg3295. PMID: 22964854.[ppl-ai-file-upload.s3.amazonaws]
-
Lynch, M. (2010). Rate, molecular spectrum, and consequences of human mutation. PNAS, 107(3), 961-968. DOI: 10.1073/pnas.0912629107. PMID: 20080596. PMC: PMC2824267.[ppl-ai-file-upload.s3.amazonaws]
-
Kondrashov, A. S. (2003). Direct estimates of human per nucleotide mutation rates at 20 loci causing Mendelian diseases. Human Mutation, 21(1), 12-27. DOI: 10.1002/humu.10147. PMID: 12497628.[ppl-ai-file-upload.s3.amazonaws]
-
Nachman, M. W., & Crowell, S. L. (2000). Estimate of the mutation rate per nucleotide in humans. Genetics, 156(1), 297-304. DOI: 10.1093/genetics/156.1.297. PMID: 10978293. PMC: PMC1461236.[ppl-ai-file-upload.s3.amazonaws]
-
Crow, J. F. (1997). The high spontaneous mutation rate: Is it a health risk? PNAS, 94(16), 8380-8386. DOI: 10.1073/pnas.94.16.8380. PMID: 9237981. PMC: PMC33757.[ppl-ai-file-upload.s3.amazonaws]
-
Muller, H. J. (1950). Our load of mutations. American Journal of Human Genetics, 2(2), 111-176. PMID: 15432463. PMC: PMC1716341.[ppl-ai-file-upload.s3.amazonaws]
-
Neel, J. V. (1998). The mutation rate and some of its implications. Evolutionary Anthropology, 6(6), 206-215. DOI: 10.1002/(SICI)1520-6505(1998)6:6<206::AID-EVAN3>3.0.CO;2-I.[ppl-ai-file-upload.s3.amazonaws]
-
Sodré Gonçalves de Brito Neto (2026). A Radiação Cósmica como Motor do Pico Mutacional Holocênico: Uma Reavaliação da Tese do Intelecto Frágil. Manuscrito Original.[ppl-ai-file-upload.s3.amazonaws]
-
Atzmon, G., et al. (2010). Abraham’s Children in the Genome Era: Major Jewish Diaspora Populations Comprise Distinct Genetic Clusters with Shared Middle Eastern Ancestry. American Journal of Human Genetics, 86(6), 850-859. DOI: 10.1016/j.ajhg.2010.04.015. PMID: 20560205. PMC: PMC3032072.[ppl-ai-file-upload.s3.amazonaws]
-
Behar, D. M., et al. (2010). The genome-wide structure of the Jewish people. Nature, 466(7303), 238-242. DOI: 10.1038/nature09103. PMID: 20531471.[ppl-ai-file-upload.s3.amazonaws]
-
Tishkoff, S. A., et al. (2009). The Genetic Structure and History of Africans and African Americans. Science, 324(5930), 1035-1044. DOI: 10.1126/science.1172257. PMID: 19407144. PMC: PMC2947357.[ppl-ai-file-upload.s3.amazonaws]
-
Li, J. Z., et al. (2008). Worldwide Human Relationships Inferred from Genome-Wide Patterns of Variation. Science, 319(5866), 1100-1104. DOI: 10.1126/science.1153717. PMID: 18292342.[ppl-ai-file-upload.s3.amazonaws]
-
Jakobsson, M., et al. (2008). Genotype, haplotype and copy-number variation in worldwide human populations. Nature, 451(7181), 998-1003. DOI: 10.1038/nature06742. PMID: 18288195.[ppl-ai-file-upload.s3.amazonaws]
-
The 1000 Genomes Project Consortium (2015). A global reference for human genetic variation. Nature, 526(7571), 68-74. DOI: 10.1038/nature15393. PMID: 26432245. PMC: PMC4750478.[ppl-ai-file-upload.s3.amazonaws]
-
Lazaridis, I., et al. (2014). Ancient human genomes suggest three ancestral populations for present-day Europeans. Nature, 513(7518), 409-413. DOI: 10.1038/nature13673. PMID: 25230653. PMC: PMC4170574.[ppl-ai-file-upload.s3.amazonaws]
-
Haak, W., et al. (2015). Massive migration from the steppe was a source for Indo-European languages in Europe. Nature, 522(7555), 207-211. DOI: 10.1038/nature14317. PMID: 25731166. PMC: PMC5048219.[ppl-ai-file-upload.s3.amazonaws]
-
Allentoft, M. E., et al. (2015). Population genomics of Bronze Age Eurasia. Nature, 522(7555), 167-172. DOI: 10.1038/nature14507. PMID: 26062507.[ppl-ai-file-upload.s3.amazonaws]
-
Mathieson, I., et al. (2015). Genome-wide patterns of selection in 230 ancient Eurasians. Nature, 528(7583), 499-503. DOI: 10.1038/nature16152. PMID: 26595274. PMC: PMC4918750.[ppl-ai-file-upload.s3.amazonaws]
-
Skoglund, P., et al. (2012). Origins and Genetic Legacy of Neolithic Farmers and Hunter-Gatherers in Europe. Science, 336(6080), 466-469. DOI: 10.1126/science.1216304. PMID: 22539720.[ppl-ai-file-upload.s3.amazonaws]
-
Raghavan, M., et al. (2014). Upper Palaeolithic Siberian genome reveals dual ancestry of Native Americans. Nature, 505(7481), 87-91. DOI: 10.1038/nature12736. PMID: 24256731. PMC: PMC4105077.[ppl-ai-file-upload.s3.amazonaws]
-
Seguin-Orlando, A., et al. (2014). Genomic structure in Europeans dating back at least 36,200 years. Science, 346(6213), 1113-1118. DOI: 10.1126/science.aaa0114. PMID: 25378462.[ppl-ai-file-upload.s3.amazonaws]
-
Olalde, I., et al. (2014). Derived immune and ancestral pigmentation alleles in a 7,000-year-old Mesolithic European. Nature, 507(7491), 225-228. DOI: 10.1038/nature12960. PMID: 24463515. PMC: PMC4118951.[ppl-ai-file-upload.s3.amazonaws]
-
Prüfer, K., et al. (2014). The complete genome sequence of a Neanderthal from the Altai Mountains. Nature, 505(7481), 43-49. DOI: 10.1038/nature12886. PMID: 24352235. PMC: PMC4031459.[ppl-ai-file-upload.s3.amazonaws]
-
Meyer, M., et al. (2012). A High-Coverage Genome Sequence from an Archaic Denisovan Individual. Science, 338(6104), 222-226. DOI: 10.1126/science.1224344. PMID: 22936568. PMC: PMC3617501.[ppl-ai-file-upload.s3.amazonaws]
-
Green, R. E., et al. (2010). A Draft Sequence of the Neandertal Genome. Science, 328(5979), 710-722. DOI: 10.1126/science.1188021. PMID: 20448196. PMC: PMC5100745.[ppl-ai-file-upload.s3.amazonaws]
-
Reich, D., et al. (2010). Genetic history of an archaic hominin group from Denisova Cave in Siberia. Nature, 468(7327), 1053-1060. DOI: 10.1038/nature09710. PMID: 21179161. PMC: PMC4306417.[ppl-ai-file-upload.s3.amazonaws]
-
Sankararaman, S., et al. (2014). The genomic landscape of Neanderthal ancestry in present-day humans. Nature, 507(7492), 354-357. DOI: 10.1038/nature12961. PMID: 24476815. PMC: PMC4072735.[ppl-ai-file-upload.s3.amazonaws]
-
Vernot, B., & Akey, J. M. (2014). Resurrecting Surviving Neandertal Lineages from Modern Human Genomes. Science, 343(6174), 1017-1021. DOI: 10.1126/science.1245938. PMID: 24476670. PMC: PMC4053333.[ppl-ai-file-upload.s3.amazonaws]
-
Fu, Q., et al. (2014). Genome sequence of a 45,000-year-old modern human from western Siberia. Nature, 514(7523), 445-449. DOI: 10.1038/nature13810. PMID: 25341783. PMC: PMC4753769.[ppl-ai-file-upload.s3.amazonaws]
-
Sodré Gonçalves de Brito Neto (2025). A Origem das Mutações: Radiação vs. Estilo de Vida. Editora Científica Independente.[ppl-ai-file-upload.s3.amazonaws]
-
Cochran, G., & Harpending, H. (2009). The 10,000 Year Explosion: How Civilization Accelerated Human Evolution. Basic Books.[ppl-ai-file-upload.s3.amazonaws]
-
Kou, S. H., et al. (2023). TP53 germline pathogenic variants in modern humans were likely originated during recent human history. NAR Cancer. DOI: 10.1093/narcancer/zcad025. PMID: 37192725.[ppl-ai-file-upload.s3.amazonaws]
-
Keane, M., et al. (2015). Insights into the Evolution of Longevity from the Bowhead Whale Genome. Cell Reports. DOI: 10.1016/j.celrep.2014.12.008. PMID: 25532846.[ppl-ai-file-upload.s3.amazonaws]
-
Seim, I., et al. (2013). Genome analysis reveals insights into physiology and longevity of the Brandt’s bat Myotis brandtii. Nature Communications. DOI: 10.1038/ncomms3212. PMID: 23963454.[ppl-ai-file-upload.s3.amazonaws]
-
Deuker, M. M., et al. (2020). Unprovoked Stabilization and Nuclear Accumulation of the p53 Protein in Naked Mole-Rat Cells. Scientific Reports. DOI: 10.1038/s41598-020-64009-0. PMID: 32332849.[ppl-ai-file-upload.s3.amazonaws]
-
Bukhman, Y. V., et al. (2024). A High-Quality Blue Whale Genome, Segmental Duplications, and Selection on Cancer-Related Genes. Molecular Biology and Evolution. DOI: 10.1093/molbev/msae036. PMID: 38381405.[ppl-ai-file-upload.s3.amazonaws]
-
Tollis, M., et al. (2019). Return to the Sea, Get Huge, Beat Cancer: An Analysis of Cetacean Genomes and Peto’s Paradox. Molecular Biology and Evolution. DOI: 10.1093/molbev/msz099. PMID: 31070746.[ppl-ai-file-upload.s3.amazonaws]
-
McGowen, M. R., et al. (2012). The genome of the bottlenose dolphin (Tursiops truncatus). Molecular Biology and Evolution. DOI: 10.1093/molbev/msr121. PMID: 21551212.[ppl-ai-file-upload.s3.amazonaws]
-
Puente, X. S., et al. (2006). Comparative analysis of cancer genes in the human and chimpanzee genomes. BMC Genomics. DOI: 10.1186/1471-2164-7-15. PMID: 16438719.[ppl-ai-file-upload.s3.amazonaws]
-
Scally, A., et al. (2012). Insights into hominid evolution from the gorilla genome sequence. Nature. DOI: 10.1038/nature10842. PMID: 22398555.[ppl-ai-file-upload.s3.amazonaws]
-
Liu, S., et al. (2014). Population genomics reveal recent speciation and rapid evolutionary adaptation in polar bears. Cell. DOI: 10.1016/j.cell.2014.03.054. PMID: 24813666.[ppl-ai-file-upload.s3.amazonaws]
-
Beklemisheva, V. R., et al. (2016). The Ancestral Carnivore Karyotype as Substantiated by Comparative Chromosome Painting. PLoS ONE. DOI: 10.1371/journal.pone.0147647. PMID: 26824345.[ppl-ai-file-upload.s3.amazonaws]
-
Zhang, G., et al. (2013). Comparative analysis of bat genomes provides insight into the evolution of flight and immunity. Science. DOI: 10.1126/science.1230835. PMID: 23258410.[ppl-ai-file-upload.s3.amazonaws]
-
Schwartz, C., et al. (2013). The p53 pathway is involved in the regulation of hibernation in ground squirrels. American Journal of Physiology. DOI: 10.1152/ajpregu.00248.2012. PMID: 22933023.[ppl-ai-file-upload.s3.amazonaws]
-
Wu, H., et al. (2014). Camelid genomes reveal evolution and adaptation to desert environments. Nature Communications. DOI: 10.1038/ncomms3720. PMID: 24220126.[ppl-ai-file-upload.s3.amazonaws]
-
Agaba, M., et al. (2016). Giraffe genome sequence reveals clues to its unique morphology and physiology. Nature Communications. DOI: 10.1038/ncomms11519. PMID: 27187143.[ppl-ai-file-upload.s3.amazonaws]
-
Kolora, S. R., et al. (2017). The genome of the white rhinoceros Ceratotherium simum. Genome Biology. DOI: 10.1186/s13059-017-1230-x. PMID: 28535798.[ppl-ai-file-upload.s3.amazonaws]
-
Vazquez, J. M., et al. (2022). Parallel evolution of reduced cancer risk and tumor suppressor duplications in Xenarthra. eLife. DOI: 10.7554/eLife.82558. PMID: 36594738.[ppl-ai-file-upload.s3.amazonaws]
-
Delsuc, F., et al. (2016). The phylogenetic affinities of the extinct glyptodonts. Current Biology. DOI: 10.1016/j.cub.2016.01.039. PMID: 26906483.[ppl-ai-file-upload.s3.amazonaws]
-
Vazquez, J. M., & Lynch, V. J. (2021). Pervasive duplication of tumor suppressors in Afrotherians. eLife. DOI: 10.7554/eLife.65041. PMID: 33646122.[ppl-ai-file-upload.s3.amazonaws]
-
Zhou, Y., et al. (2021). Platypus and echidna genomes reveal mammalian biology and evolution. Nature. DOI: 10.1038/s41586-020-03039-0. PMID: 33408411.[ppl-ai-file-upload.s3.amazonaws]
-
Warren, W. C., et al. (2008). Genome analysis of the platypus reveals unique signatures of evolution. Nature. DOI: 10.1038/nature06936. PMID: 18464734.[ppl-ai-file-upload.s3.amazonaws]
-
Epstein, B., et al. (2016). Rapid evolutionary response to a transmissible cancer in Tasmanian devils. Nature Communications. DOI: 10.1038/ncomms12684. PMID: 27572564.[ppl-ai-file-upload.s3.amazonaws]
-
Johnson, R. N., et al. (2018). Adaptation and conservation insights from the koala genome. Nature Genetics. DOI: 10.1038/s41588-018-0153-5. PMID: 29967444.[ppl-ai-file-upload.s3.amazonaws]
-
Mikkelsen, T. S., et al. (2007). Genome of the marsupial Monodelphis domestica reveals innovation in non-coding sequences. Nature. DOI: 10.1038/nature05805. PMID: 17495919.[ppl-ai-file-upload.s3.amazonaws]
-
Nery, M. F., et al. (2016). Genomic signatures of positive selection in the Amazonian manatee. Molecular Biology and Evolution. DOI: 10.1093/molbev/msw261. PMID: 27927787.[ppl-ai-file-upload.s3.amazonaws]
-
Dudchenko, O., et al. (2021). The genome of the dugong Dugong dugon. Scientific Reports. DOI: 10.1038/s41598-021-95435-x. PMID: 34349156.[ppl-ai-file-upload.s3.amazonaws]
-
Heaton, M. P., et al. (2015). Dispersal of an ancient retroposon in the TP53 promoter of Bovidae. BMC Genomics. DOI: 10.1186/s12864-015-1235-8. PMID: 25622741.[ppl-ai-file-upload.s3.amazonaws]
-
Selvarajah, G. T., et al. (2015). TP53 mutations in canine osteosarcoma. Veterinary and Comparative Oncology. DOI: 10.1111/vco.12122. PMID: 25611434.[ppl-ai-file-upload.s3.amazonaws]
-
Levine, A. J. (1997). p53, the cellular gatekeeper for growth and division. Cell, 88(3), 323-331. DOI: 10.1016/S0092-8674(00)81871-1. PMID: 9039259.[ppl-ai-file-upload.s3.amazonaws]
-
Feng, Z., et al. (2007). Declining p53 function in the aging process: a possible mechanism for the increased tumor incidence in older populations. PNAS, 104(42), 16633-16638. DOI: 10.1073/pnas.0708043104. PMID: 17925444. PMC: PMC2034252.[ppl-ai-file-upload.s3.amazonaws]
-
Guo, J., et al. (2022). Aging and aging-related diseases: from molecular mechanisms to interventions. Signal Transduction and Targeted Therapy, 7(1), 391. DOI: 10.1038/s41392-022-01251-0. PMID: 36522308. PMC: PMC9755446.[ppl-ai-file-upload.s3.amazonaws]
-
Ou, H. L., & Schumacher, B. (2018). DNA damage responses and p53 in the aging process. Blood, 131(5), 488-495. DOI: 10.1182/blood-2017-07-746396. PMID: 29141943. PMC: PMC6839964.[ppl-ai-file-upload.s3.amazonaws]
-
Mijit, M., et al. (2020). Role of p53 in the Regulation of Cellular Senescence. Biomolecules, 10(3), 420. DOI: 10.3390/biom10030420. PMID: 32182984. PMC: PMC7175209.[ppl-ai-file-upload.s3.amazonaws]
-
Estrutura Proposta para o Artigo Científico
1. Introdução
Compreendido. Analisei o texto anterior e refiz a explicação para dar o destaque solicitado à capacidade de previsão como elemento central, e para detalhar os resultados possíveis de um teste: o acerto (corroboração), o erro (falsificação) e a evasão (hipóteses ad hoc).
A abordagem a seguir reestrutura o conceito, colocando o poder preditivo no coração da filosofia da ciência de Popper.
A Ciência como um Motor de Previsões Arriscadas
Para entender a distinção entre falseabilidade e teste, é mais eficaz começar com a ideia de que uma teoria científica não é apenas uma explicação para o que já aconteceu, mas sim um motor para prever o que irá acontecer. O valor de uma teoria está diretamente ligado à qualidade e à ousadia de suas previsões.
É neste contexto que os conceitos de falseabilidade, teste, corroboração, falsificação e hipóteses ad hoc se encaixam.
1. Falseabilidade: A Qualidade Preditiva da Teoria
A falseabilidade não é sobre a teoria estar errada; é sobre sua capacidade de fazer previsões específicas e arriscadas. Uma teoria é falseável se suas previsões proíbem que certos eventos aconteçam. É essa proibição que dá conteúdo empírico à teoria e a torna testável.
- Função: Avaliar o poder preditivo de uma teoria. Uma teoria que não proíbe nada, não prevê nada.
- Pergunta-chave: “Que previsões específicas esta teoria faz que, se não se confirmarem, a invalidarão?”
Exemplos de Poder Preditivo (e Falseabilidade):
- Alto Poder Preditivo (Falseável): A Teoria da Relatividade Geral de Einstein previu que a luz de uma estrela distante se curvaria ao passar perto do Sol numa quantidade específica (aproximadamente 1.75 segundos de arco). Esta é uma previsão incrivelmente arriscada. Ela proíbe que a luz não se curve ou que se curve numa quantidade diferente.
- Baixo Poder Preditivo (Não-Falseável): A afirmação “Eventos cósmicos influenciam seu destino”. Esta afirmação não proíbe nenhum evento específico na vida de uma pessoa. Qualquer acontecimento (bom ou mau) pode ser interpretado como uma “influência cósmica”, tornando a previsão imune à refutação.
2. Teste: O Confronto com a Realidade
O teste é o ato de verificar se as previsões arriscadas de uma teoria se concretizam no mundo real. É o processo empírico de observar se os eventos que a teoria proibiu de fato não acontecem.
O resultado de um teste leva a três cenários principais, que revelam o status da teoria:
Os Três Resultados de um Teste Preditivo
Resultado 1: A Previsão se Confirma (Corroboração)
Quando uma previsão arriscada e específica se mostra correta, a teoria é corroborada.
- O que significa: A teoria sobreviveu a uma tentativa séria de refutação. Sua credibilidade e seu status como a melhor explicação disponível aumentam significativamente. Corroboração não é “prova” definitiva, mas sim um forte selo de aprovação empírica.
- Exemplo Clássico: Em 1919, a expedição de Arthur Eddington observou um eclipse solar e confirmou que a luz das estrelas se curvava na quantidade exata prevista por Einstein. A Teoria da Relatividade não foi “provada”, mas foi poderosamente corroborada. A previsão de um acerto em um teste tão severo demonstrou seu imenso poder explicativo.
- Exemplo do Criacionismo Terra Jovem: Previu tempo curto dos fosseis e se encontrou mais de 1200 fosseis contendo tecidos orgânicos; Combateu datações radiométricas baseadas em constância de decaimento, Carpinteri et e tal confirmaram aceleração e de caimento (envelhecimento de rochas) pelos efeitos piezolétricos , plasmas, fono-fissão, que em circunstâncias de efeitos globais de grandes impactos . +73 exemplos de previsões acertadas
Resultado 2: A Previsão Falha (Falsificação ou Refutação)
Quando uma previsão clara da teoria se mostra incorreta, a teoria é falsificada.
- O que significa: A teoria, em sua forma atual, está errada. Um único erro genuíno em uma previsão fundamental é suficiente para refutar a teoria inteira (do ponto de vista lógico). A ciência progride ao descartar teorias falsificadas e buscar novas que expliquem tanto o que a antiga explicava quanto a anomalia que a refutou.
- Exemplo Clássico: A teoria de que “Todos os planetas se movem em órbitas circulares perfeitas” fazia uma previsão clara sobre a trajetória dos planetas. As observações meticulosas de Tycho Brahe e a análise de Johannes Kepler mostraram que Marte se movia numa elipse. A previsão do círculo falhou, e a teoria foi falsificada, abrindo caminho para as Leis de Kepler.
Resultado 3: A Previsão Falha, mas a Teoria é “Salva” (Hipótese Ad Hoc)
Este é o cenário que muitas vezes distingue a ciência da pseudociência. Quando uma previsão falha, em vez de abandonar a teoria, seus defensores introduzem uma modificação ou uma nova premissa especificamente para salvar a teoria daquela refutação. Isso é uma hipótese ad hoc.
- O que significa: É uma manobra defensiva que “imuniza” a teoria contra a crítica. O problema de uma hipótese ad hoc é que ela geralmente não gera novas previsões testáveis; ela apenas explica a falha anterior. Isso reduz o poder preditivo e a falseabilidade da teoria. Para Popper, o uso contínuo de hipóteses ad hoc é a marca de um programa de pesquisa degenerativo (não-científico).
- Exemplo Clássico: A Teoria do Flogisto afirmava que materiais combustíveis continham uma substância chamada “flogisto”, que era liberada durante a queima. Uma previsão dessa teoria é que um material deveria perder massa ao ser queimado. No entanto, experimentos mostraram que metais ganhavam massa ao serem calcinados (queimados).
- Falsificação: Isso deveria ter refutado a teoria.
- Manobra Ad Hoc: Para salvar a teoria, alguns defensores propuseram que o flogisto tinha “massa negativa”. Essa hipótese explicava perfeitamente a anomalia observada, mas foi criada ad hoc (para este propósito) e não fazia nenhuma nova previsão arriscada. Era um remendo, não um avanço. A teoria estava, na prática, sendo falseada, mas seus defensores se recusavam a aceitar.
Tabela Comparativa com Foco em Previsão
| Característica | Falseabilidade | Teste Científico |
|---|---|---|
| Foco Principal | Poder Preditivo: A capacidade de fazer previsões arriscadas que proíbem resultados. | Confronto Preditivo: A execução de um experimento para ver se a previsão se sustenta. |
| Natureza | Lógica e teórica (a qualidade da teoria). | Empírica и prática (a ação sobre a teoria). |
| Resultado para a Teoria | Classifica a teoria como científica (se tiver poder preditivo) ou não. | Leva a um de três resultados práticos para a previsão. |
| Resultados Possíveis do Teste | N/A | 1. Corroboração (previsão correta)2. Falsificação (previsão errada)3. Hipótese Ad Hoc (tentativa de salvar a teoria da falsificação) |
Em resumo, a falseabilidade dota uma teoria com a capacidade de fazer previsões que podem dar certo ou errado. O teste é o que determina qual desses caminhos a realidade segue, e a reação a uma previsão errada (aceitar a falsificação ou inventar uma desculpa ad hoc) separa a prática científica rigorosa da dogmática.

Deixe um comentário